Luigi Ricciardi 1 , Rosa Mazzeo 2,*©, Angelo Raffaele Marcotrigiano 1 , Guglielmo Rainaldi 3 , Paolo Iovieno 4 , Vito Zonno 1 , Stefano Pavan 1 © u Concetta Lotti 2,*
- 1 Dipartiment tax-Xjenzi tal-Ħamrija, Pjanti u Ikel, Ġenetika tal-Pjanti u Unità tat-Tnissil Università ta’ Bari, Via Amendola 165/A, 70125 Bari, l-Italja; luigi.ricciardi@uniba.it (LR);angelo.marcotrigiano@uniba.it (ARM); vito.zonno@uniba.it (VZ); stefano.pavan@uniba.it (SP)
- 2 Dipartiment tax-Xjenzi tal-Agrikoltura, Ikel u Ambjent, Università ta' Foggia, Via Napoli 25, 71122 Foggia, l-Italja
- 3 Dipartiment tal-Bijoxjenzi, Bijoteknoloġiji u Bijofarmaċewtiċi, Università ta’ Bari, Via Orabona 4, 70125 Bari, l-Italja; guglielmo.rainaldi@uniba.it
- 4 Dipartiment tat-Teknoloġiji tal-Enerġija, Bijoenerġija, Bijoraffinerija u Green Chemistry Division, ENEA Trisaia Research Center, SS 106 Ionica, km 419+500, 75026 Rotondella (MT), l-Italja; paolo.iovieno@enea.it
* Korrispondenza: rosa.mazzeo@unifg.it (RM); concetta.lotti@unifg.it (CL)
Astratt:
Onion (Allium cepa L.) hija t-tieni uċuħ tal-ħxejjex l-aktar importanti madwar id-dinja u hija apprezzata ħafna għall-benefiċċji għas-saħħa tagħha. Minkejja l-importanza ekonomika sinifikanti tagħha u l-valur tagħha bħala ikel funzjonali, il-basla ġiet investigata ħażin fir-rigward tad-diversità ġenetika tagħha. Hawnhekk, aħna stħarreġna l-varjazzjoni ġenetika fil-"Basla ħamra Acquaviva" (ARO), landa bi storja ta 'seklu ta' kultivazzjoni f'belt żgħira fil-provinċja ta 'Bari (Apulia, Nofsinhar tal-Italja). Intużaw sett ta' 11-il markatur mikrosatelliti biex jesploraw il-varjazzjoni ġenetika f'kollezzjoni ta' ġermoplasma li tikkonsisti fi 13-il popolazzjoni ARO u tliet tipi kummerċjali komuni. Analiżi tal-istruttura ġenetika b'metodi parametriċi u mhux parametriċi enfasizzaw li l-ARO jirrappreżenta ġabra ta' ġeni definita sew, distinta b'mod ċar mir-razzetti tal-pajjiż Tropea u Montoro li ħafna drabi jiżbalja magħhom. Sabiex tiġi pprovduta deskrizzjoni tal-bozoz, normalment użati għall-konsum frisk, ġew evalwati kontenut solidu solubbli u pikkanti, li juru ħlewwa ogħla fl-ARO fir-rigward taż-żewġ razzetti tal-pajjiż imsemmija hawn fuq. B'mod ġenerali, l-istudju preżenti huwa utli għall-valorizzazzjoni futura tal-ARO, li tista' tiġi promossa permezz ta' tikketti ta' kwalità li jistgħu jikkontribwixxu biex jillimitaw il-frodi kummerċjali u jtejbu d-dħul tal-bdiewa ż-żgħar.
introduzzjoni
Il-ġeneru Allium jinkludi madwar 750 speċi [1], fosthom il-basla (Allium cepa L., 2n = 2x =16) hija waħda mill-aktar mifruxa. A. cepa għandu ċiklu ta' kull sentejn u mġiba riproduttiva ta' qsim. Illum il-ġurnata, il-produzzjoni globali tal-basal (97.9 Mt) tagħmilha t-tieni uċuħ tal-ħxejjex l-aktar importanti wara t-tadam [2]. Minn żminijiet antiki, il-basal tal-basal intużaw kemm bħala ikel kif ukoll f'applikazzjonijiet mediċinali folkloristiċi. Tabilħaqq, l-Eġizzjani tal-qedem diġà rrappurtaw diversi formuli terapewtiċi bbażati fuq l-użu tat-tewm u l-basal f'papyrus mediku tal-1550 QK, il-Codex Ebers [3].
Dan il-ħaxix versatili u b'saħħtu huwa kkunsmat nej, frisk, jew bħala prodott ipproċessat, u użat biex itejjeb it-togħma ta 'ħafna platti. Diversi studji reċenti jsostnu li l-konsum tal-basal jista 'jnaqqas ir-riskju ta' mard kardjovaskulari [4,5], obeżità [6], dijabete [7], u diversi forom ta 'kanċer [8-10]. Il-propjetajiet tas-saħħa tal-basal ħafna drabi huma attribwiti għal livelli għoljin ta 'żewġ klassijiet ta' komposti nutraċewtiċi: flavonoids u alk(en)yl cysteine sulphoxides (ACSOs). L-ewwel klassi tinkludi flavonols u anthocyanins. Quercetin huwa l-flavonol li jista' jinqabad ewlieni, magħruf għall-proprjetajiet anti-ossidanti u anti-infjammatorji qawwija tiegħu fit-tneħħija tar-radikali ħielsa u l-irbit tal-joni tal-metalli ta' transizzjoni. [11]; billi anthocyanins jagħtu kulur aħmar/vjola lil xi varjetajiet ta' basal. Fir-rigward tal-ACSOs, l-aktar abbundanti huwa isoalliin [(+)-trans-S-1-propenyl-L-cysteine sulfoxide] [12], aċidu amminiku tal-kubrit mhux volatili u mhux proteinoġeniku maħżun fiċ-ċelloli, li huwa indirettament responsabbli għall-aroma punġenti u t-togħma tal-basal [13]. Meta tfixkel it-tessut, isoalliin jinqasam mill-enzima alliinase biex jipproduċi serje ta 'komposti volatili (pyruvate, ammonja, thiosulphonates u propanethial S-oxide) li jinduċu dmugħ u jikkawżaw riħa spjaċevoli (pungency) [14]. Il-pikanenza tal-basal ħafna drabi titkejjel bħala l-ammont, għal kull gramma ta’ piż frisk, ta’ aċidu piruviku ġġenerat mill-idroliżi [15,16].
Fil-pajjiżi tal-baċir tal-Mediterran, propost bħala wieħed miċ-ċentri tad-diversità sekondarji ta A. cepa [17,18], il-bozoz tal-basal juru varjabbiltà wiesgħa fil-forma, id-daqs, il-kulur, il-materja niexfa u l-pungency [19-waħda]. Barra minn hekk, il-fertilizzazzjoni bbażata fuq il-kubrit, il-prattiki agronomiċi, it-tip ta’ ħamrija, il-kundizzjonijiet klimatiċi, u l-ġenotip tal-kultivari jew tar-razzetti tal-post jistgħu jinfluwenzaw il-kwalità tal-bozza billi jagħtu valuri organolettiċi u nutrittivi partikolari. [23-waħda]. Fl-Italja, minkejja d-disponibbiltà wiesgħa tal-ġermoplasma tal-basal, ftit varjetajiet ta’ basla biss huma spiss soġġetti għal studji xjentifiċi u kkaratterizzati sew [28,29].
Karatterizzazzjoni ġenetika u fenotipika bir-reqqa tal-agro-bijodiversità hija kruċjali biex tiġi żgurata l-konservazzjoni xierqa tar-riżorsi ġenetiċi tal-pjanti u jiġi promoss l-użu ta’ ġenotipi speċifiċi fil-katina tal-valur [30-waħda]. Markers sempliċi sequence repeat (SSR) spiss intgħażlu għall-immappjar [33-waħda], marki tas-swaba tad-DNA u diskriminazzjoni tal-kultivari [36-waħda], u stima affidabbli tal-varjabbiltà ġenetika fi ħdan u fost razez tal-pajjiż [39-waħda], peress li huma speċifiċi għal locus, multi-alleliċi, wirtu b'mod codominant, riproduċibbli ħafna, u adattati għal ġenotipi awtomatizzati.
Fl-istudju preżenti, aħna ffukajna l-attenzjoni tagħna fuq razza tradizzjonali ta’ Apulia, il-“Basla ħamra Acquaviva” (ARO), li hija kkultivata skont metodi ta’ biedja organika f’żona żgħira tal-belt ta’ Acquaviva delle Fonti, fil-provinċja ta’ Bari. (Apulija, Nofsinhar tal-Italja). Il-bozoz ta’ din ir-razza huma kbar u ċċattjati u ta’ kulur aħmar u jintużaw ħafna fir-riċetti lokali. Għalkemm l-ARO kisbet il-marka ta’ kwalità “Slow Food Presidium”, il-produzzjoni tagħha tista’ tiġi promossa u protetta aktar minn marki ta’ kwalità tal-Unjoni Ewropea bħal indikazzjoni ġeografika protetta (IĠP) u denominazzjoni protetta tal-oriġini (POD), peress li dawn jistgħu jikkontribwixxu biex jillimitaw il- frodi kummerċjali u jtejjeb id-dħul tal-proprjetarji żgħar. Hawnhekk, il-markaturi molekulari SSR intużaw bħala għodda qawwija biex tiġi vvalutata l-varjazzjoni ġenetika fost il-popolazzjonijiet ARO u biex jiddiskriminaw din ir-razza minn żewġ tipi oħra tal-basal aħmar tan-Nofsinhar Taljan. Barra minn hekk, stmajna kontenut solidu pikkanti u solubbli sabiex nevalwaw it-togħma ARO b'relazzjoni mad-domanda tas-suq.
Riżultati
Twaqqif tal-Ġbir tal-Ġermoplasm tal-Basal Ħamra Acquaviva u Karatterizzazzjoni Morfoloġika
Żrieragħ ta' 13-il popolazzjoni tar-razza ARO, mogħtija minn bdiewa fil-qafas tal-proġett tar-Reġjun BiodiverSO Apulia intużaw biex tiġi stabbilita kollezzjoni ta' ġermoplasma ARO.
Deskritturi morfoloġiċi, relatati mal-bozza, il-ġilda, u l-laħam inġabru fuq il-ġermoplasma ARO u fuq tliet razzets tal-basal, tnejn li jappartjenu għall-"basla ħamra Tropea" (TRO) u waħda għall-"basla tar-ram Montoro" (MCO) (Figura 1). Il-bozoz ARO kollha kienu ċatti u kienu kkaratterizzati minn ġilda esterna u laħam aħmar bi sfumaturi differenti ta 'aħmar. B'kuntrast, il-laħam tal-bozoz TRO kien aħmar għal kollox, filwaqt li l-laħam tal-bozoz MCO kien pigmentat ħażin (Tabella S1). Analiżi bijokimika ppermettiet li tevalwa l-kontenut solubbli solidu u pungency. Kif irrappurtat fit-Tabella 1, il-valuri medji tal-kontenut solubbli solidu tal-bozoz fil-popolazzjonijiet ARO kien 7.60, u varjaw minn 6.00 (ARO12) sa 9.50° Brix (ARO11 u ARO13). Dan il-valur kien ogħla minn dak stmat għall-gruppi TRO u MCO (4.25 u 6.00° Brix, rispettivament).

Tabella 1. Kontenut Solubbli Solidu u Valuri Punġenti Vvalutati f'Popolazzjonijiet "Acquaviva Red Onion" (ARO), "Tropea Red Onion" (TRO), u "Montoro Copper Onion" (MCO) *.
| KODIĊI | Kontenut Solidu Solubbli (Brix) | Punġenza (pmolg-1 FW) | ||
| Medja | CV y (%) | Medja | CV y (%) | |
| ARO1 | 6.25 D * | 5.65 | 5.84 ab * | 23.78 |
| ARO2 | 7.25 DC | 4.87 | 6.51 a | 22.98 |
| ARO3 | 7.50 BCD | 9.42 | 5.28ab | 22.88 |
| ARO4 | 7.50 BCD | 0.00 | 6.97 a | 3.74 |
| ARO 5 | 7.50 BCD | 0.00 | 6.80 a | 9.68 |
| ARO6 | 6.25 D | 5.65 | 4.51ab | 39.18 |
| ARO7 | 7.25 DC | 4.87 | 5.25ab | 15.44 |
| ARO8 | 9.00 AB | 0.00 | 7.04 a | 3.49 |
| ARO9 | 8.25 ABC | 4.28 | 6.84 a | 0.15 |
| ARO10 | 7.00 DC | 0.00 | 5.94ab | 6.57 |
| ARO11 | Il 9.50 | 7.44 | 5.54ab | 16.43 |
| ARO12 | 6.00 D | 0.00 | 4.91ab | 9.70 |
| ARO13 | Il 9.50 | 7.44 | 6.63 a | 24.93 |
| MCO | 6.00 D | 0.00 | 4.18ab | 2.66 |
| TRO1 | 4.25 E | 8.31 | 2.80 b | 2.10 |
| TRO2 | 4.25 E | 8.31 | 4.28ab | 4.79 |
* Mezzi bl-istess ittri b'ittri kbar jew żgħar mhumiex statistikament differenti f'0.01P jew 0.05P, rispettivament (Test ta' SNK). y Koeffiċjent tal-varjazzjoni.
Il-valur medju ta 'ARO pungency, evalwat permezz tal-kontenut ta' aċidu piruviku, kien 6.00, varja minn 4.51 pmol g-1 FW (ARO6) sa 7.04 (ARO8). Dan il-valur kien ogħla minn dak stmat f’razez lokali TRO u MCO (3.54 pmol g-1 FW u 4.18 pmol g-1 FW, rispettivament).
Polimorfiżmu SSR u Relazzjonijiet Ġenetiċi fost Adeżjonijiet....
Fl-istudju preżenti, 11 minn 37 kombinazzjoni ta 'primer SSR ittestjati pprovdew polimorfiżmi ta' locus wieħed, jiġifieri, li jipproduċu l-aktar żewġ prodotti ta 'amplifikazzjoni f'individwu wieħed. B'mod ġenerali, ġew skoperti 55 alleli fi 320 individwu b'numru ta' alleli għal kull locus li jvarja minn 2 (ACM147 u ACM 504) sa 11 (ACM132) u valur medju ta' 5 alleli (Tabella 2). F'popolazzjonijiet individwali, in-numru ta 'alleli (Na) varja minn 1.94 (ACM147 u ACM504) sa 5.38 (ACM132), filwaqt li n-numru effettiv ta' alleli (Ne) varja minn 1.41 (ACM152) sa 2.82 (ACM449). Diskrepanzi bejn il-valuri ta' Na u Ne kienu dovuti għall-preżenza ta' alleli bi frekwenza baxxa fil-popolazzjonijiet u l-predominanza ta' ftit alleli biss. L-ogħla valur osservat ta' eterozigożità (Ho) kien enfasizzat għal ACM138 u ACM449 (0.62), filwaqt li l-iktar wieħed baxx kien assoċjat ma' ACM152 (0.25). L-eterozigożità mistennija (He), li tikkorrispondi mal-aspettattiva teoretika f'popolazzjoni panmictika, varjat minn 0.37 (ACM504) sa 0.61 (ACM132, ACM138, u ACM449). L-indiċi ta' fissazzjoni ta' Wright (Fis), wera valuri qrib iż-żero (medja ta' 0.05) għall-markaturi kollha, li jindika valuri simili bejn il-livelli ta' eterozigożità osservati u mistennija, kif mistenni għal speċi ta' qsim. L-effiċjenza ta 'markatur SSR individwali fil-marki tas-swaba' ġenetiċi ġiet stmata mill-indiċi tal-kontenut ta 'informazzjoni polimorfika (PIC), b'valur medju ta' 0.48 u varjat minn 0.33 (ACM504) għal 0.67 (ACM132). Indiċi ieħor ta 'effiċjenza, l-Indiċi ta' Informazzjoni ta 'Shannon (I) wera valur medju ta' 0.84, u valuri assunti varjaw minn 0.45 (ACM152) għal 1.20 (ACM132).
Tabella 2. Karatteristiċi tal-polimorfiżmu tal-11-il Marker SSR Użati biex Tistma d-Diversità Ġenetika f'Popolazzjonijiet ARO, TRO u MCO. Numru Totali ta 'Alleli (Na), Medda ta' Daqs tal-Banda, u Indiċi tal-Kontenut ta 'Informazzjoni Polimorfika (PIC) Irreferi għas-Sett Totali ta' 320 Individwi Ġenotipati f'dan l-Istudju. Numru ta' Alleles (Na), numru ta' Alleles Effettivi (Ne), Eterozigożità Osservata (Ho), Eterozigożità Mistennija (He), Indiċi ta' Fissa (Fis), u l-Indiċi ta' Informazzjoni ta' Shannon (I) jirreferu għal Valuri Medji Ikkalkulati minn 16-il Popolazzjoni, Kull Magħmul minn 20 Individwi.
| Locus. | Total Na | Firxa Daqs (bp) | PIC | Medja | |||||
| Na | Ne | Ho | He | I | Fis | ||||
| ACM91 | 4 | 189-205 | 0.40 | 2.63 | 1.72 | 0.38 | 0.39 | 0.66 | 0.04 |
| ACM101 | 4 | 229-241 | 0.52 | 2.94 | 2.37 | 0.53 | 0.56 | 0.92 | 0.06 |
| ACM132 | 11 | 186-248 | 0.67 | 5.38 | 2.78 | 0.55 | 0.61 | 1.20 | 0.09 |
| ACM138 | 5 | 242-272 | 0.66 | 3.69 | 2.82 | 0.62 | 0.61 | 1.09 | -0.02 |
| ACM147 | 2 | 264-266 | 0.37 | 1.94 | 1.83 | 0.44 | 0.44 | 0.62 | -0.01 |
| ACM152 | 4 | 228-244 | 0.25 | 2.38 | 1.41 | 0.25 | 0.27 | 0.45 | 0.07 |
| ACM235 | 4 | 286-298 | 0.41 | 2.81 | 1.77 | 0.44 | 0.41 | 0.72 | -0.06 |
| ACM446 | 6 | 108-120 | 0.56 | 3.50 | 2.48 | 0.49 | 0.58 | 1.01 | 0.16 |
| ACM449 | 8 | 120-140 | 0.66 | 4.88 | 2.82 | 0.62 | 0.61 | 1.18 | -0.03 |
| ACM463 | 5 | 202-210 | 0.47 | 3.38 | 1.95 | 0.46 | 0.48 | 0.83 | 0.05 |
| ACM504 | 2 | 188-192 | 0.33 | 1.94 | 1.64 | 0.30 | 0.37 | 0.54 | 0.20 |
| Medja | 5 | 0.48 | 3.22 | 2.15 | 0.46 | 0.48 | 0.84 | 0.05 |
Fost il-popolazzjonijiet, ARO3, ARO6, ARO8, ARO10, TRO1, u MCO wrew livell għoli ta 'varjazzjoni ġenetika (Ho> 0.5), filwaqt li l-inqas diversità kienet osservata fil-popolazzjoni ARO7 (Ho = 0.27) (Tabella Supplimentari S2). B'mod ġenerali, l-adeżjonijiet kollha wrew Fis valuri qrib iż-żero (Fis valur medju = 0.054), kif mistenni taħt kundizzjonijiet ta 'tgħammir każwali.
Analiżi ta' Varjanza Molekulari u Struttura Ġenetika
Il-qsim ġerarkiku tal-varjazzjoni ġenetika fost u fi ħdan il-popolazzjonijiet ġie kkalkulat minn AMOVA. Ir-riżultati enfasizzaw frazzjoni konsiderevoli ta 'varjazzjoni ġenetika fi ħdan il-popolazzjonijiet (87%). Varjazzjoni fost il-popolazzjonijiet, 13%, kienet sinifikanti ħafna (P < 0.001) (Tabella 3). Il-valuri f'pari tal-parametru Fpt, analogu għall-indiċi ta' fissazzjoni Fst ta' Wright, li jvarjaw minn 0.002 (ARO2/ARO10) sa 0.468 (ARO7/TRO2), kienu sinifikanti (P < 0.05), ħlief għal disa' paraguni f'pari (Tabella Supplimentari S3).
Tabella 3. Analiżi ta' Varjanza Molekulari ta' 320 Ġenotipi minn 16-il Popolazzjoni ta' allium cepa L.
| sors | df | Somma ta 'Pjazez | Stima ta' Varjazzjoni | Varjazzjoni (%) | Fpt | P |
| Fost popolazzjonijiet | 15 | 458.63 | 1.16 | 13% | ||
| Fi ħdan il-popolazzjonijiet | 304 | 2272.99 | 7.50 | 87% | 0.134 | 0.001 |
| total | 319 | 2731.62 | 8.66 |
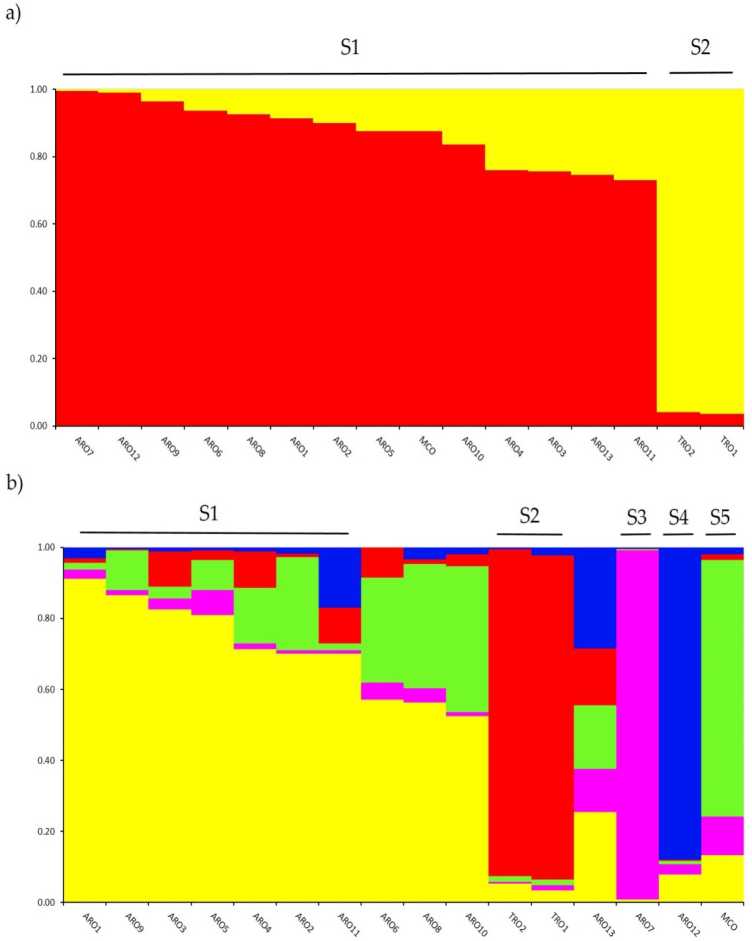
Investigazzjoni ta 'struttura ġenetika fil- A. cepa il-ġbir ġenotipat f'dan l-istudju sar permezz tal-analiżi tal-clustering ibbażata fuq il-mudell tat-taħlita implimentata fl-ISTRUTTURA tas-softwer. Il-metodu Evanno AK issuġġerixxa suddiviżjoni f'żewġ gruppi (K = 2) bħala l-aktar informattiv għal tagħna sett tad-dejta,ma 'the li jmiss ogħla peak at K = 5 (Supplimentaiv Rgure S1). A għal K = 2, ahpopulazzjonijiet were ħmarigned biex onuf iż-żewġ gruppi ma a rnernbertoip koeffiċjent (q) > 0.7. Kif shown fi Figura 2a, l-ewwel cluster (imsemmi S1) inkluda l-MCO u l-popolazzjonijiet ARO kollha, filwaqt li l-cluster S2 raggruppa ż-żewġ popolazzjonijiet TRO. F'K = 5, tipprovdi deskrizzjoni aktar profonda tas-sett tad-dejta (Figura 2b), 75 % tal-adeżjonijiet ġew assenjati għal wieħed mill-ħames cluster. Separazzjoni bejn ARO (S1) u TRO (S2) ġiet ikkonfermata, għalkemm xi popolazzjonijiet ARO ġew imħallta (q <0.7) jew miġbura separatament fiż-żewġ gruppi ġodda S3 u S4 (ARO7 u ARO12, rispettivament). Interessanti, it-tip kummerċjali MCO ifforma raggruppament distint (S5) separat mill-basla ħamra Apulian.
Relazzjonijiet Ġenetiċi fost Popolazzjonijiet
Il-polimorfiżmu SSR ippermetta li jiġbed dendrogramma tad-diversità ġenetika u r-riżultati tal-analiżi filoġenetika huma murija fil-Figura 3a. Hawnhekk, il-kollezzjoni tal-ġermoplasma kienet maqsuma f'ħames gruppi appoġġjati b'mod qawwi minn valuri bootstrap. Il-popolazzjonijiet ARO7 u ARO12 ġew immedjatament separati mill-popolazzjonijiet li kien fadal u ffurmaw żewġ gruppi distinti. It-tielet raggruppament inkluda ż-żewġ popolazzjonijiet kummerċjali ta 'TRO, sadanittant ir-raba' nodu qasam MCO minn ħdax-il popolazzjoni ARO. Ir-relazzjoni ġenetika li sseħħ fost il-popolazzjonijiet ġiet investigata aktar permezz ta 'analiżi tal-koordinati prinċipali (PCoA) (Figura 3b). Kif enfasizzat qabel, il-popolazzjonijiet ARO ġew miġbura sewwa, ħlief għal ARO12 u ARO7, li dehru f'pożizzjonijiet iżolati fil-plott PCoA. Iż-żewġ TROs u l-popolazzjonijiet MCO kienu mxerrda fil-pannell ta 'isfel tal-lemin tal-plott.
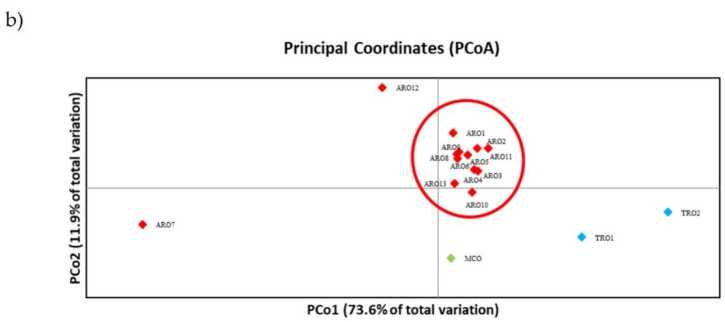
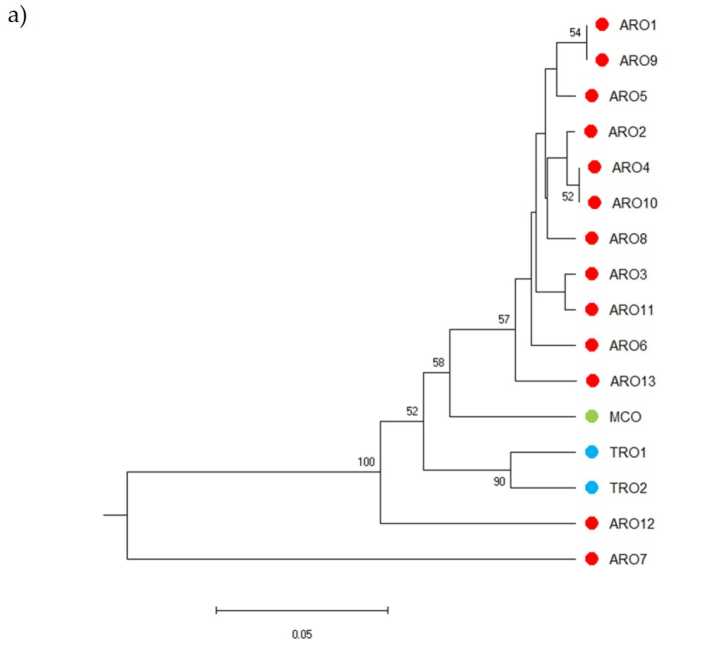
Figura 3. Diversità ġenetika fost 16 A. cepa popolazzjonijiet ikkaratterizzati f'dan l-istudju, ibbażati fuq il-profil SSR tagħhom. (a) Dendrogramma UPGMA tad-distanza ġenetika. Valuri ta 'appoġġ Bootstrap> 50 huma indikati fuq in-nodi korrispondenti; (b) analiżi tal-komponenti prinċipali (PCoA). Il-cluster imdawwar bl-aħmar qabbel bis-sħiħ mal-grupp iġġenerat mill-analiżi filoġenetika u kkostitwit minn 11-il adeżjoni ARO.
Diskussjoni
Fi ħdan l-ammont kbir ta 'agro-bijodiversità tradizzjonalment ikkultivata fin-Nofsinhar tal-Italja, il-landraces tal-basal jirrappreżentaw prodotti niċċa li jeħtieġ li jiġu ppreservati mir-riskju ta' erożjoni ġenetika u t-theddida ta 'sostituzzjoni minn kultivari moderni. Fil-qafas tal-proġett reġjonali BiodiverSO, immirat li jiġbor, jikkaratterizza, jippromwovi, u jissalvagwardja r-riżorsi ġenetiċi tar-reġjun tal-Apulia marbuta b'mod qawwi mal-wirt lokali, waqqafna ġabra ta 'żerriegħa ta' 13-il popolazzjoni tar-razza ARO. Aħna rrapportajna l-ewwel valutazzjoni tal-varjazzjoni ARO f'termini ta 'polimorfiżmi tad-DNA u żewġ parametri bijokimiċi, kontenuti ta' solidu solubbli u aċidu piruviku, relatati mal-karatteristiċi tat-togħma u ta 'importanza għall-aċċettazzjoni tal-prodotti friski mhux imsajra. Barra minn hekk, id-dejta dwar il-landrace ARO tqabbel ma 'dawk miġbura fuq żewġ landraces tal-basal pigmentati oħra li ħafna drabi żbaljat magħhom.
Analiżi bijokimiċi enfasizzaw il-ħlewwa tat-13-il popolazzjoni ARO, relatata ma 'kontenut solidu solubbli għoli u pungenza medja, skont il-linji gwida tal-industrija tal-basal ħelu [31]. Il-bozoz ARO kienu ħelwin minn dawk tat-tro u MCO landraces, u wrew pungency kemmxejn ogħla. Madankollu, il-ħlewwa fil-basal hija dovuta għal bilanċ bejn il-kontenut taz-zokkor u l-pikanezza, għalhekk din il-karatterizzazzjoni tista 'tkun utli biex tappoġġja l-għażla ta' ġenotipi ta 'valur, normalment imwettqa mill-bdiewa bbażati biss fuq il-morfoloġija.
Markers SSR ġew ikkonfermati li huma għodda utli biex jiddiskriminaw il-ġenotipi, għalkemm miġbura f'żona dejqa ta' tkabbir bħall-belt ta' Acquaviva delle Fonti. Il-markaturi magħżula wrew numru ogħla ta' alleli mill-markaturi rrappurtati qabel [43] u, [44], iżda inqas mill-markaturi rrappurtati minn [45]. Barra minn hekk, 50% tas-sett tagħna ta 'markaturi wrew valuri tal-indiċi PIC akbar minn 0.5, u wrew li huma adattati biex jiddiskriminaw il-popolazzjonijiet fil-ġbir, kif issuġġerit minn [46]. Il-valutazzjoni tad-diversità fi ħdan il-popolazzjonijiet żvelat valuri simili bejn Ho u He, li rriżultaw f'Fi baxxs valuri. Dan huwa bi qbil man-natura ta 'out-crossing A. cepa, li jbati serjament minn dipressjoni ta’ inbreeding [47]. Il-Fi ġeneralis valur ikkalkulat fil-popolazzjonijiet tal-basal ikkunsidrati f'dan l-istudju (0.054) kien inqas minn dak irrappurtat qabel minn [45] (0.22) u kważi identiku għal dak misjub minn [31] (0.08) u [48] (0.00) li evalwaw id-diversità ġenetika f'races tal-basal mill-majjistral ta' Spanja u n-Niġer, rispettivament. Livelli notevoli ta’ eterozigożità fil-popolazzjonijiet ARO isaħħu l-idea li Apulia tirrappreżenta ċentru ta’ diversità għal ħafna speċi ortikulturali [32, 42, 49-waħda].
AMOVA enfasizzat li l-biċċa l-kbira tal-varjazzjoni molekulari fil-ġabra ġenotipata f'dan l-istudju tinsab fi ħdan il-popolazzjonijiet. Madankollu, differenzazzjoni ġenetika sinifikanti fost il-popolazzjonijiet (FPT valuri) żvelat l-okkorrenza ta 'stratifikazzjoni ġenetika. Fil-fatt, għalkemm ir-riżultati tagħna indikaw il-preżenza ta 'uniformità ġenetika fil-biċċa l-kbira tal-popolazzjonijiet ARO, li jiffurmaw cluster definit tajjeb, il-popolazzjonijiet ARO7 u ARO12 wrew profil ġenetiku distint b'mod ċar. Dan ir-riżultat jista’ jkun dovut għal oriġini differenti taż-żrieragħ użati miż-żewġ bdiewa li minnhom inġabru l-popolazzjonijiet. Barra minn hekk, abbażi tar-riżultati miksuba, ir-razza ARO tista' titqies b'mod ċar distinta fil-livell ġenetiku mir-razza TRO u MCO. Fi studju riċenti, [29] ivvaluta d-diversità ġenetika ta’ diversi tipi tal-basal Taljani inklużi “Acquaviva”, “Tropea” u “Montoro”. Għalkemm l-awturi użaw markaturi SNP biex jevalwaw id-diversità ġenetika ta 'ġbir usa' tal-basal, il-ġenotipi ma kienx kapaċi jiddiskrimina "Acquaviva" minn basal "Tropea" u "Montoro". Probabbilment, din id-diskrepanza hija dovuta għall-valur PIC medju baxx misjub (0.292), li jissuġġerixxi informazzjoni ġenerali modesta tal-loċi taħt analiżi kif iddikjarat minn [29]. Barra minn hekk, sabiex tiġi investigata l-preżenza tas-sottostruttura fil-cluster Taljan tagħhom, kien ikun aħjar li jiġu analizzati l-ġenotipi Taljani separatament mill-bqija tal-kollezzjoni. Probabbilment kien ippermetta li wieħed jivviżwalizza mudell ta 'diversità ġenetika marbuta ma' stratifikazzjoni ġeografika jew karatteristiċi taħt għażla empirika.
Bħala konklużjoni, l-istudju preżenti jirrappreżenta rapport komprensiv dwar razza tal-basal assoċjata mal-wirt kulturali lokali u ta’ importanza ekonomika għall-bdiewa. Ir-riżultati tagħna jenfasizzaw li, bi ftit eċċezzjonijiet, ARO huwa kkaratterizzat minn ġabra ta 'ġeni definita sew, li jistħoqqilha li tiġi ppreservata mir-riskju ta' erożjoni ġenetika. Għalhekk, it-twaqqif ta’ kollezzjoni rappreżentattiva ta’ dan is-sors prezzjuż ta’ diversità ġenetika kien kruċjali. Fl-aħħar nett, il-karatterizzazzjoni ġenetika u fenotipika ta' ARO tista' tkun utli biex jinkisbu marki ta' kwalità mill-Unjoni Ewropea.
Materjali u Metodi
Ġbir Ġemoplasma, Materjal tal-Pjanti, u Estrazzjoni tad-DNA
Ġew akkwistati sett ta’ 13-il popolazzjoni tar-razza ARO fi ħdan il-qafas ta’ proġett tar-Reġjun tal-Apulia (BiodiverSO: https://www.biodiversitapuglia.it/), permezz ta’ sensiela ta’ missjonijiet imwettqa f’“Acquaviva delle Fonti”, belt żgħira tal-Apulija fil-Provinċja ta’ Bari, l-Italja. Is-siti tal-ġbir ta' kull adeżjoni ġew immappjati permezz tas-Sistema ta' Informazzjoni Ġeografika (GIS) u rrapportati fit-Tabella 4. Barra minn hekk, żewġ popolazzjonijiet mir-razza TRO u popolazzjoni waħda mill-MCO ġew inklużi fl-istudju preżenti u użati bħala referenzi. Il-materjal tal-pjanti kollu tkabbar fl-istess kundizzjonijiet ambjentali fir-razzett sperimentali “P Martucci” tal-Università ta’ Bari (41° 1'22.08″ N, 16°54'25.95″ E), taħt gaġġa ta’ protezzjoni biex tiġi evitata pollinazzjoni inkroċjata fost popolazzjonijiet u l-iżgurar ta' pollinazzjoni intra-popolazzjoni permezz ta' blowflies (Lucilia caesar). Is-16-il popolazzjoni kienu kkaratterizzati għal karatteristiċi relatati mad-daqs u l-għamla tal-bozza u l-ġilda u l-kulur tal-laħam (Tabella S1). Barra minn hekk, l-assaġġ tal-kontenut solidu solubbli twettaq bl-użu ta 'refrattometru li jinżamm fl-idejn u tkejjel il-pungenza f'kampjuni ta' meraq tal-basal li żiedu 2,4-dinitrophenyl hydrazine (0.125% v/v f'2N ta' HCl) u jevalwaw l-assorbiment f'420 nm, kif irrappurtat minn [31]. It-test ta' firxa multipla ta' Duncan u t-test SNK twettqu biex jiddeterminaw il-preżenza ta' differenzi sinifikanti.
Tabella 4. Lista ta' Popolazzjonijiet Miġbura u Ġenotipati f'Dan l-Istudju. Għal Kull Popolazzjoni, Kodiċi ta' Identifikazzjoni, Isem Lokali, Koordinati tal-GPS, u Bank tal-Ġene li Jippreserva ż-Żrieragħ huma Rapportati.
| kodiċi | isem | Koordinati GPS | Bank tal-Ġeni y |
| ARO1 | Cipolla rossa di Acquaviva | 40°54’21.708″ N 16°49’1.631” E | Di.SSPA |
| ARO2 | Cipolla rossa di Acquaviva | 40°53’14.28″ N 16°48’56.879” E | Di.SSPA |
| ARO3 | Cipolla rossa di Acquaviva | 40°54’11.304″ N 16°49’13.079” E | Di.SSPA |
| ARO4 | Cipolla rossa di Acquaviva | 40°54’3.348″ N 16°40’27.011” E | Di.SSPA |
| ARO5 | Cipolla rossa di Acquaviva | 40°51’59.76″ N 16°53’0.527” E | Di.SSPA |
| ARO6 | Cipolla rossa di Acquaviva | 40°52’48.72″ N 16°49’43.247” E | Di.SSPA |
| ARO7 | Cipolla rossa di Acquaviva | 40°53’13.47″ N 16°50’23.783” E | Di.SSPA |
| ARO8 | Cipolla rossa di Acquaviva | 40°53’18.816″ N 16°49’33.888” E | Di.SSPA |
| ARO9 | Cipolla rossa di Acquaviva | 40°54"51.372″ N 16°49"3.504" E | Di.SSPA |
| ARO10 | Cipolla rossa di Acquaviva | 40°54’1.188″ N 16°49’24.311” E | Di.SSPA |
| ARO11 | Cipolla rossa di Acquaviva | 40°52"49.8″ N 16°49"48.575" E | Di.SSPA |
| ARO12 | Cipolla rossa di Acquaviva | 40°52’38.892″ N 16°49’28.379” E | Di.SSPA |
| ARO13 | Cipolla rossa di Acquaviva | 40°53’21.768″ N 16°49’29.711” E | Di.SSPA |
| TRO1 | Cipolla rossa lunga di Tropea | - | Di.SSPA |
| TRO2 | Cipolla rossa tonda di Tropea | - | Di.SSPA |
| MCO | Cipolla ramata di Montoro | - | Di.SSPA |
| y Di.SSPA, Dipartiment tax-Xjenzi tal-Ħamrija, tal-Pjanti u tal-Ikel, Università ta' Bari. |
Materjal tal-weraq ta '20 ġenotip għal kull popolazzjoni ġew kampjunati u maħżuna f'-80 °C sakemm jintuża. Għal speċi b'ħafna polisakkaridi, kif A. cepa, l-ewwel passi li jneħħu l-polysaccharide huma essenzjali biex jinkiseb DNA ta' kwalità tajba, għalhekk ħasliet inizjali fil-buffer STE (0.25 M sukrożju, 0.03 M Tris, 0.05 M EDTA) saru kif deskritt minn [52]. Id-DNA totali ġie estratt skont il-metodu CTAB [53] u finalment ġie ċċekkjat għall-kwalità u l-konċentrazzjoni minn Nano Drop 2000 UV-vis spectrophotometer (ThermoScientific, Waltham, MA, USA) u 0.8% agarose gel electrophoresis.
Analiżi SSR
16 kombinazzjonijiet primer EST-SSR żviluppati minn [54] u ttestjati qabel fi studji dwar id-diversità ġenetika minn [43] u, [44] u 21 SSR ġenomika [45-waħda] ġew skrinjati biex jevalwaw l-adegwatezza tagħhom (Tabella Supplimentari S4). Il-ġenotipar sar bl-użu tal-metodu ta' tikkettar fluworexxenti ekonomiku li fih id-denb M13 huwa miżjud ma' kull primer SSR 'il quddiem [56]. Taħlitiet ta’ PCR ġew ippreparati f’reazzjoni ta’ 20 gL li kien fihom: 50 ng ta’ DNA totali, 0.2 mM ta’ taħlita dNTP, 1X ta’ buffer ta’ reazzjoni PCR, 0.8 U ta’ DreamTaq DNA polymerase (Thermo Scientific, Waltham, MA, USA), 0.16 gM ta’ reverse primer , 0.032 gM ta 'primer bil-quddiem estiż bis-sekwenza M13 (5′-TGTAAAACGACGGCCAGT-3′), u 0.08 gM ta' primer M13 universali ttikkettjat b'żebgħat fluworexxenti FAM jew NED (Sigma-Aldrich, St. Louis, MO, USA). Ir-reazzjonijiet tal-PCR twettqu fit-termoċiklu SimpliAmp (Applied Biosystems, CA, USA) bil-kundizzjonijiet li ġejjin għall-maġġoranza tal-pari primer: 94 °C għal 5 min, 40 ċiklu f'94 °C għal 30 s, 58 °C għal 45 s u 72 °C għal 45 s u elongazzjoni finali f'72 °C għal 5 min. Fir-rigward tal-ACM446 u l-ACM449, ġiet applikata PCR tal-illandjar b'ttemprar ta '60 °C sa 55 °C fuq 10 ċikli, 30 ċiklu f'55 °C, segwit minn estensjoni finali ta' 5 min f'72 °C. Il-prodotti tal-PCR ġew mgħobbija fi pjanċa 96-well u mħallta ma '14 gL ta' Hi-Di Formamide (Teknoloġiji tal-Ħajja, Carlsbad, CA, USA) u 0.5 gL GeneScan 500 ROX Size Standard (Teknoloġiji tal-Ħajja, Carlsbad, CA, USA). L-amplicons ġew solvuti permezz ta 'magna ta' sekwenzar kapillari ABI PRISM 3100 Avant Genetic Analyzer (Life Technologies, Carlsbad, CA, USA), fejn l-alleli ġew skurjati bħala ko-dominanti u assenjati bl-użu tal-GeneMapper Software Version 3.7.
Is-softwares GenAlEx 6.5 [57] u Cervus 3.0.7 [58] intużaw biex jistmaw in-numru ta' alleli (Na), in-numru ta' alleli effettivi (Ne), eterozigożità osservata (Ho), eterozigożità mistennija (He), kontenut ta' informazzjoni polimorfika (PIC), indiċi ta' informazzjoni ta' Shannon (I), u indiċi ta' fissazzjoni (Fis). ) għal kull locus SSR.
Valutazzjoni tad-Diversità Ġenetika
Il-qsim ġerarkiku tal-varjazzjoni ġenetika fost u fi ħdan il-popolazzjonijiet tal-basal ġie evalwat minn GenAlEx 6.5 [57] permezz tal-analiżi tal-varjanza molekulari (AMOVA) b'999 bootstrapping biex tittestja s-sinifikat. Barra minn hekk, is-softwer GenAlEx 6.5 intuża biex jistma d-diversità f'kull popolazzjoni billi kkalkola l-medja ta 'Ho, He, u Fis fuq il-loċi SSR kollha.
L-istruttura tal-popolazzjoni ġiet dedotta mill-algoritmu ta' clustering ibbażat fuq mudell Bayesjan implimentat fis-softwer STRUCTURE v.2.3.4 [59]. Is-sett tad-dejta tmexxa b'numru ta 'clusters ipotetiċi (K), li jvarjaw minn 1 sa 10, li jistabbilixxu għaxar ġirjiet indipendenti għal kull valur K. Għal kull ġirja, bil-għan li tivverifika l-konsistenza tar-riżultati, twettqu 100,000 perjodu inizjali ta 'ħruq u 100,000 iterazzjoni Markov Chain Monte Carlo (MCMC) taħt il-mudell ta' taħlita u frekwenzi ta 'allele indipendenti fost il-popolazzjonijiet. L-iktar valur K probabbli ġie determinat bl-implimentazzjoni tal-metodu AK, deskritt minn [60], fil-programm ibbażat fuq il-web STRUCTURE HARVESTER [61]. Popolazzjoni individwali ġiet assenjata għal raggruppament speċifiku meta l-koeffiċjent ta 'sħubija tagħha (valur q) kien ogħla minn 0.7, inkella kienet ikkunsidrata ta' antenati mħallta.
Twettqet analiżi tal-koordinati prinċipali sabiex jiġu viżwalizzati mudelli ta 'relazzjoni ġenetika fost l-adeżjonijiet żvelati mill-matriċi tad-distanza ġenetika tan-Nei (Tabella Supplimentari S5). Ibbażat fuq il-frekwenzi tal-alleli, inbniet dendrogramma ta' distanza ġenetika li timplimenta l-metodu ta' grupp ta' par mhux ippeżat b'analiżi ta' clusters ta' medji aritmetiċi (UPGMA) fis-softwer POPTREEW [62]. Bootstrapping ġie applikat biex tiġi vvalutata l-kunfidenza fir-raggruppament ġerarkiku, billi stabbiliet kampjunar mill-ġdid ta '100 tas-sett tad-dejta. Fl-aħħarnett, softwer MEGA X [63] intuża bħala softwer għat-tpinġija tas-siġar.
Materjali Supplimentari: Dawn li ġejjin huma disponibbli online fuq http://www.mdpi.com/2223-7747/9/2/260/s1. Tabella S1: Karatterizzazzjoni morfoloġika tal-bozoz ARO, MCO, u TRO. Tabella S2: Indiċijiet ta' eterozigożità u ta' fissazzjoni kkalkulati għal razzetti tal-pajjiż ARO u razzetti tal-pajjiż TRO u MCO. Tabella S3: Valuri f'pari tal-parametru Fpt. Tabella S4: Lista tal-SSRs użati fl-istudju. Tabella S5. Matriċi tal-popolazzjoni f'pari ta' distanza ġenetika Nei. Figura S1: Grafika tal-linji tal-valuri K li jinbidlu bid-Delta K ta’ Evano.
Kontribuzzjonijiet tal-awtur: CL u LR ikkonċepiw l-istudju u ddisinjaw l-esperiment; CL u PI wettqu analiżi tal-markatur molekulari; ARM u VZ wettqu l-provi fuq il-post; RM, SP, GR, u CL kienu involuti fl-analiżi tad-dejta; RM u CL kitbu l-manuskritt. L-awturi kollha qraw u qablu mal-verżjoni ppubblikata tal-manuskritt.
Finanzjament: Dan ix-xogħol kien iffinanzjat mill-proġett Reġjonali Apulian "Bijodiversità ta 'speċi veġetali Apulian"—Programma di Sviluppo Rurale per la Puglia 2014-2020. Misura 10—Sottomisura 10.2; għotja CUP H92C15000270002, l-Italja.
rikonoxximenti: Rikonoxximenti huma dovuti lil “Azienda Agricola Iannone Anna” u “Associazione produttori della vera cipolla rossa di Acquaviva” talli pprovdew materjali tal-pjanti użati fl-esperiment.
Konflitti ta 'Interess: L-awturi ma jiddikjaraw l-ebda kunflitt ta 'interess.
Referenzi
- 1. Stearn, WT Kemm huma magħrufa speċi ta' Allium? Kew Mag. 1992, 9,180-182. [CrossRef]
- 2. FAOSTAT. Database tal-Istatistika tal-FAO. Disponibbli onlajn: http://www.fao.org/2017 (aċċessat fit-8 ta’ Jannar 2019).
- 3. Blokk, E. Il-kimika tat-tewm u l-basla. Sci. Em. 1985, 252,114-119. [CrossRef]
- 4. Lee, B.; Jung, JH; Kim, HS Valutazzjoni tal-basla ħamra fuq l-attività antiossidanti fil-far. Chem tal-Ikel. Tossikol. 2012, 50, 3912-3919. [CrossRef]
- 5. Lee, SM; Qamar, J.; Chung, JH; Cha, YJ; Shin, MJ Effett ta 'estratti tal-qoxra tal-basal b'ħafna quercetin fuq trombożi arterjali fil-firien. Chem tal-Ikel. Tossikol. 2013, 57, 99-105. [CrossRef] [PubMed]
- 6. Yoshinari, O.; Shiojima, Y.; Igarashi, K. Effetti kontra l-obeżità ta 'estratt tal-basal fil-firien grassi dijabetiċi zucker. nutrijenti 2012, 4,1518-1526. [CrossRef]
- 7. Akash, MSH; Rehman, K.; Chen, S. Spice plant Allium cepa: Suppliment tad-dieta għat-trattament tad-dijabete mellitus tat-tip 2. Nutrizzjoni 2014, 30,1128-1137. [CrossRef] [PubMed]
- 8. Wang, Y.; Tian, WX; Ma, XF Effetti Inibitorji tal-basla (Allium cepa L.) estratt fuq il-proliferazzjoni ta 'ċelluli tal-kanċer u adipocytes permezz ta' inibizzjoni ta 'aċidu xaħmi synthase. Pac Asjatiku. J. Kanċer Prev. 2012,13, 5573-5579. [CrossRef] [PubMed]
- 9. Lai, WW; Hsu, SC; Chueh, FS; Chen, YY; Yang, JS; Lin, JP; Lien, JC; Tsai, CH; Chung, JG Quercetin jinibixxi l-migrazzjoni u l-invażjoni taċ-ċelluli tal-kanċer orali tal-bniedem SAS permezz ta 'inibizzjoni ta' mogħdijiet ta 'sinjalazzjoni NF-kappaB u matrix metalloproteinase-2/-9. Kontra l-kanċer Res. 2013, 33,1941-1950. [PubMed]
- 10. Nicastro, HL; Ross, SA; Milner, JA Tewm u basal: Il-proprjetajiet tagħhom għall-prevenzjoni tal-kanċer. Kanċer Prev. Riż. 2015, 8,181-189. [CrossRef]
- 11. Forte, L.; Torricelli, P.; Boanini, E.; Gazzano, M.; Rubini, K.; Fini, M.; Bigi, A. Proprjetajiet antiossidanti u ta 'tiswija ta' l-għadam ta 'hydroxyapatite funzjonalizzat bil-quercetin: Studju ta' ko-kultura ta 'ċelluli osteoblast-osteoclast-endoteljali in vitro. Acta Biomater. 2016, 32, 298-308. [CrossRef]
- 12. Yamazaki, Y.; Iwasaki, K.; Mikami, M.; Yagihashi, A. Distribuzzjoni ta 'ħdax-il prekursuri tat-togħma, derivattivi S-Alk(en)yl-L-cysteine, f'seba' ħxejjex Allium. Ikel Sci. Technol. Riż. 2011, 17, 55-62. [CrossRef]
- 13. Blokk, E. Il-kimika ta 'l-organosulfur tal-Genus Allium—Implicazzjonijiet għall-kimika organika tal-kubrit. Angew. Chem. Int. Ed. Engl. 1992, 31,1135-1178. [CrossRef]
- 14. Griffiths, G.; Trueman, L.; Crowther, T.; Thomas, B.; Smith, B. Basal-Benefiċċju globali għas-saħħa. Phytother. Riż. 2002,16, 603-615. [CrossRef]
- 15. Schwimmer, S.; Weston, WJ Żvilupp enżimatiku ta 'aċidu piruviku fil-basla bħala miżura ta' pungency. J. Agri. Chem tal-Ikel. 1961, 9, 301-304. [CrossRef]
- 16. Ketter, CAT; Randle, WM Valutazzjoni pungency fil-basal. Fil Studji Ittestjati għat-Tagħlim fil-Laboratorju; Karcher, SJ, Ed.; Assoċjazzjoni għall-Edukazzjoni tal-Laboratorju tal-Bijoloġija (ABLE): New York, NY, USA, 1998; Volum 19, pp. 177-196.
- 17. Hanelt, P Tassonomija, evoluzzjoni u storja. Fil Basal u Crops Alleati, Vol. I. Botanika, Fiżjoloġija u Ġenetika; Rabinowitch, HD, Brewster, JL, Eds.; CRC Press: Boca Raton, FL, USA, 1990; pp. 1-26.
- 18. Rabinowitch, HD; Currah, L. Allium Crop Science: Avvanzi Riċenti; Pubblikazzjoni CABI: Wallingford, UK, 2002.
- 19. Mallor, C.; Carravedo, M.; Estopanan, G.; Mallor, F. Karatterizzazzjoni tar-riżorsi ġenetiċi tal-basal (Allium cepa L.) miċ-ċentru sekondarju Spanjol tad-diversità. Span. J. Agri. Riż. 2011, 9,144-155. [CrossRef]
- 20. Ferioli, F.; D'Antuono, LF Evalwazzjoni ta 'fenoliċi u sulfossidi taċ-ċisteina fil-basal lokali u l-ġersoplażma tal-basal mill-Italja u l-Ukrajna. Genet. Riżors. Crop Evol. 2016, 63, 601-614. [CrossRef]
- 21. Petropoulos, SA; Fernandes, A.; Barros, L.; Ferreira, ICFR; Ntatsi, G. Deskrizzjoni morfoloġika, nutrittiva u kimika ta' 'vatikiotiko', razza lokali tal-basal mill-Greċja. Chem tal-Ikel. 2015,182,156-163. [CrossRef]
- 22. Liguori, L.; Adiletta, G.; Nazzaro, F.; Fratianni, F.; Di Matteo, M.; Albanese, D. Bijokimiċi, proprjetajiet antiossidanti u attività antimikrobika ta 'varjetajiet ta' basla differenti fiż-żona tal-Mediterran. J. Ikel Meas. Karattru. 2019,13,1232-1241. [CrossRef]
- 23. Yoo, KS; Pike, L.; Crosby, K.; Jones, R.; Leskovar, D. Differenzi fil-pungency tal-basal minħabba kultivari, ambjent ta 'tkabbir, u daqsijiet tal-bozoz. Sci. Ortiku. 2006,110,144-149. [CrossRef]
- 24. Beesk, N.; Perner, H.; Schwarz, D.; Ġorġ, E.; Kroh, LW; Rohn, S. Distribuzzjoni ta 'quercetin-3, 4'-O-diglucoside, quercetin-4'-O-monoglucoside, u quercetin f'partijiet differenti tal-bozza tal-basal (Allium cepa L.) influwenzati mill-ġenotip. Chem tal-Ikel. 2010,122, 566-571. [CrossRef]
- 25. Caruso, G.; Konti, S.; Villari, G.; Borrelli, C.; Melchionna, G.; Minutolo, M.; Russo, G.; Amalfitano, C. Effetti tal-ħin tat-trapjant u d-densità tal-pjanti fuq ir-rendiment, il-kwalità u l-kontenut antiossidant tal-basla (Allium cepa L.) fin-Nofsinhar tal-Italja. Sci. Ortiku. 2014,166,111-120. [CrossRef]
- 26. Perez-Gregorio, MR; Regueiro, J.; Simal-Gandara, J.; Rodrigues, AS; Almeida, DPF Żieda fil-valur miżjud tal-basal bħala sors ta 'flavonoids antiossidanti: Reviżjoni kritika. Krit. Rev Ikel Sci. Nutr. 2014, 54,1050-1062. [CrossRef] [PubMed]
- 27. Pohnl, T.; Schweigert, RM; Carle, R. Impatt tal-metodu tal-kultivazzjoni u l-għażla tal-kultivari fuq karboidrati solubbli u prinċipji punġenti fil-basal (Allium cepa L.). J. Agri. Chem tal-Ikel. 2018, 66,12827-12835. [CrossRef] [PubMed]
- 28. Tedesco, I.; Carbone, V.; Spagnuolo, C.; Minasi, P.; Russo, GL Identifikazzjoni u kwantifikazzjoni ta 'flavonoids minn żewġ kultivari tan-Nofsinhar Taljan ta' allium cepa L., Tropea (basla ħamra) u Montoro (basla tar-ram), u l-kapaċità tagħhom li jipproteġu l-eritroċiti umani minn stress ossidattiv. J. Agri. Chem tal-Ikel. 2015, 63, 5229-5238. [CrossRef]
- 29. Villano, C.; Esposito, S.; Carucci, F.; Frusciante, L.; Carputo, D.; Aversano, R. Il-ġenotipar b'rendiment għoli fil-basla jiżvela struttura tad-diversità ġenetika u SNPs informattivi utli għat-tnissil molekulari. Mol. Razza. 2019, 39, 5. [CrossRef]
- 30. Mercati, F.; Longo, C.; Poma, D.; Araniti, F.; Lupini, A.; Mammano, MM; Fiore, MC; Abenavoli, MR; Sunseri, F Varjazzjoni ġenetika ta' tadam Taljan ta' żmien twil fuq l-ixkaffa (Solanum lycopersicum L.) ġbir billi tuża SSR u karatteristiċi morfoloġiċi tal-frott. Genet. Riżors. Crop Evol. 2014, 62, 721-732. [CrossRef]
- 31. Gonzalez-Perez, S.; Mallor, C.; Garces-Claver, A.; Merino, F.; Taboada, A.; Rivera, A.; Pomar, F.; Perovic, D.; Silvar, C. Jesploraw id-diversità ġenetika u l-karatteristiċi ta 'kwalità f'kollezzjoni ta' basla.... (Allium cepa L.) razez tal-post mill-majjistral ta' Spanja. Ġenetika 2015, 47, 885-900. [CrossRef]
- 32. Lotti, C.; Iovieno, P.; Centomani, I.; Marcotrigiano, AR; Fanelli, V.; Mimiola, G.; Summo, C.; Pavan, S.; Ricciardi, L. Karatterizzazzjoni ġenetika, bijo-agronomika u nutrizzjonali tal-kale (brassica oleracea L. var. acephala) id-diversità fl-Apulia, fin-Nofsinhar tal-Italja. Diversità 2018,10, 25. [CrossRef]
- 33. Bardaro, N.; Marcotrigiano, AR; Bracuto, V.; Mazzeo, R.; Ricciardi, F.; Lotti, C.; Pavan, S.; Ricciardi, L. Analiżi ġenetika tar-reżistenza għal Orobanche crenata (Forsk.) f’piżelli (Pisum sativum L.) linja ta 'strigolactone baxx. J. Pathol tal-Pjanti. 2016, 98, 671-675.
- 34. Wako, T.; Tsukazaki, H.; Yaguchi, S.; Yamashita, K.; Ito, S.; Shigyo, M. Immappjar ta 'loċi ta' karatteristiċi kwantitattivi għall-ħin tal-bolting fil-basla tal-għenieqed (Allium fistulosum L.). Euphytica 2016, 209, 537-546. [CrossRef]
- 35. Dhaka, N.; Mukhopadhyay, A.; Paritosh, K.; Gupta, V.; Pental, D.; Pradhan, AK Identifikazzjoni ta 'SSRs ġeniċi u kostruzzjoni ta' mappa ta 'rabta bbażata fuq SSR fi Brassica juncea. Euphytica 2017, 213, 15. [CrossRef]
- 36. Anandhan, S.; Mote, SR; Gopal, J. Evalwazzjoni tal-identità varjetali tal-basal bl-użu ta 'markaturi SSR. Żerriegħa Sci. Technol. 2014, 42, 279-285. [CrossRef]
- 37. Mitrova, K.; Svoboda, P.; Ovesna, J. L-għażla u l-validazzjoni ta 'sett ta' markatur għad-divrenzjar tal-kultivari tal-basal mir-Repubblika Ċeka. Ċek J. Genet. Razza tal-Pjanti. 2015, 51, 62-67. [CrossRef]
- 38. Di Rienzo, V.; Miazzi, MM; Fanelli, V.; Sabetta, W.; Montemurro, C. Il-preservazzjoni u l-karatterizzazzjoni tal-bijodiversità tal-ġermoplasma taż-żebbuġ Apulian. Acta Hortic. 2018,1199,1-6. [CrossRef]
- 39. Mallor, C.; Arnedo-Andres, A.; Garces-Claver, A. Evalwazzjoni tad-diversità ġenetika tal-Ispanjol allium cepa landraces għat-trobbija tal-basal bl-użu ta' markaturi mikrosatelliti. Sci. Ortiku. 2014,170,24-31. [CrossRef]
- 40. Rivera, A.; Mallor, C.; Garces-Claver, A.; Garcia-Ulloa, A.; Pomar, F.; Silvar, C. Valutazzjoni tad-diversità ġenetika fil-basla (allium cepa L.) razez mill-majjistral ta' Spanja u tqabbil mal-varjabbiltà Ewropea. NZJ Crop Hortic. 2016, 44,103-120. [CrossRef]
- 41. De Giovanni, C.; Pavan, S.; Taranto, F.; Di Rienzo, V.; Miazzi, MM; Marcotrigiano, AR; Mangini, G.; Montemurro, C.; Ricciardi, L.; Lotti, C. Varjazzjoni ġenetika ta 'ġbir ta' ġermoplasma globali taċ-ċiċri.... (Cicer arietinum L.) inklużi adeżjonijiet Taljani f'riskju ta' erożjoni ġenetika. Physiol. Mol. Biol. Pjanti 2017, 23,197-205. [CrossRef]
- 42. Mazzeo, R.; Morgese, A.; Sonnante, G.; Zuluaga, DL; Pavan, S.; Ricciardi, L.; Lotti, C. Id-diversità ġenetika fil-brokkoli rabe (Brassica rapa L. subsp. sylvestris (L.) Janch.) min-Nofsinhar tal-Italja. Sci. Ortiku. 2019, 253,140-146. [CrossRef]
- 43. Jakse, M.; Martin, W.; McCallum, J.; Havey, M. Polimorfiżmi ta' nukleotidi wieħed, indels, u ripetizzjonijiet ta' sekwenza sempliċi għall-identifikazzjoni tal-kultivari tal-basal. J. Am. Soc. Ortiku. Sci. 2005,130, 912-917. [CrossRef]
- 44. McCallum, J.; Thomson, S.; Pither-Joyce, M.; Kenel, F. Analiżi tad-diversità ġenetika u żvilupp ta 'markatur ta' polimorfiżmu ta 'nukleotide wieħed f'basla tal-bozza kkultivata bbażata fuq markaturi ripetuti ta' sekwenza sempliċi ta 'sekwenza espressa. J. Am. Soc. Ortiku. Sci. 2008,133, 810-818. [CrossRef]
- 45. Baldwin, S.; Pither-Joyce, M.; Wright, K.; Chen, L.; McCallum, J. Żvilupp ta’ markaturi ta’ ripetizzjoni ta’ sekwenza sempliċi ġenomika robusta għall-istima tad-diversità ġenetika fi ħdan u fost il-basla tal-bozza (Allium cepa L.) popolazzjonijiet. Mol. Razza. 2012, 30,1401-1411. [CrossRef]
- 46. DeWoody, JA; Honeycutt, RL; Skow, LC Markers mikrosatelliti fiċ-ċriev ta' denbu abjad. J. Hered. 1995, 86, 317-319. [CrossRef] [PubMed]
- 47. Khodadadi, M.; Hassanpanah, D. Basla Iranjana (Allium cepa L.) tweġibiet tal-kultivari għad-dipressjoni tal-inbreeding. Dinjija Appl. Sci. J. 2010,11, 426-428.
- 48. Abdou, R.; Bakasso, Y.; Saadou, M.; Baudoin, JP; Hardy, ĠU Diversità ġenetika tal-basal tan-Niġer (Allium cepa L.) evalwati b'markaturi sempliċi ta' sekwenza ripetuta (SSR). Acta Hortic. 2016,1143, 77-90. [CrossRef]
- 49. Pavan, S.; Lotti, C.; Marcotrigiano, AR; Mazzeo, R.; Bardaro, N.; Bracuto, V.; Ricciardi, F.; Taranto, F.; D'Agostino, N.; Schiavulli, A.; et al. Raggruppament ġenetiku distint fiċ-ċiċri kkultivati kif żvelat mill-iskoperta u l-ġenotipi tal-markaturi mal-ġenoma kollu. Ġenoma tal-Pjanti 2017, 2017,10. [CrossRef]
- 50. Pavan, S.; Marcotrigiano, AR; Ciani, E.; Mazzeo, R.; Zonno, V.; Ruggieri, V.; Lotti, C.; Ricciardi, L. Genotyping-by-sequencing of a bettieħa (Cucumis melo L.) ġbir ta 'ġermoplasma minn ċentru sekondarju ta' diversità jenfasizza mudelli ta 'varjazzjoni ġenetika u karatteristiċi ġenomiċi ta' ġabriet ta 'ġeni differenti. BMC Genom. 2017, 18, 59. [CrossRef]
- 51. Di Rienzo, V.; Sion, S.; Taranto, F.; D'Agostino, N.; Montemurro, C.; Fanelli, V.; Sabetta, W.; Boucheffa, S.; Tamendjari, A.; Pasqualone, A.; et al. Fluss ġenetiku fost il-popolazzjoni taż-żebbuġ fil-baċir tal-Mediterran. Peer J. 2018, 6. [CrossRef]
- 52. Ragħaj, LD; McLay, TG Żewġ protokolli fuq skala mikro għall-iżolament tad-DNA minn tessut tal-pjanti b'ħafna polisakkaridi. J. Pjanti Res. 2011,124, 311-314. [CrossRef]
- 53. Doyle, JJ; Doyle, JL Iżolament tad-DNA tal-pjanti minn tessut frisk. Iffoka 1990,12,13-14.
- 54. Kuhl, JC; Cheung, F.; Qiaoping, Y.; Martin, W.; Zewdie, Y.; McCallum, J.; Catanach, A.; Rutherford, P.; Jegħrqu, KC; Jenderek, M.; et al. Sett uniku ta '11,008 tikketti tas-sekwenza espressi tal-basal jiżvela sekwenza espressa u differenzi ġenomiċi bejn l-ordnijiet monocot asparagales u poales. Ċellula tal-Pjanti 2004,16, 114-125. [CrossRef]
- 55. Kim, HJ; Lee, HR; Hyun, JY; Kanzunetta, KH; Kim, KH; Kim, JE; Hur, CG; Harn, CH Marker żvilupp għall-ittestjar tal-purità ġenetika tal-basal bl-użu tal-SSR Finder. Korean J. Razza. Sci. 2012, 44, 421-432. [CrossRef]
- 56. Schuelke, M. Metodu ekonomiku għall-ittikkettar fluworexxenti tal-frammenti tal-PCR. Nat. Bijoteknoloġija. 2000, 18, 233-234. [CrossRef] [PubMed]
- 57. Peakall, R.; Smouse, PE GenAlEx 6.5: Analiżi ġenetika f'Excel. Softwer ġenetiku tal-popolazzjoni għat-tagħlim u r-riċerka: Aġġornament. Bijoinformatika 2012, 28, 2537-2539. [CrossRef] [PubMed]
- 58. Kalinowski, ST; Taper, ML; Marshall, TC Ir-reviżjoni ta' kif il-programm tal-kompjuter CERVUS jakkomoda l-iżball tal-ġenotipjar iżid is-suċċess fl-assenjazzjoni tal-paternità. Mol. Ekol. 2007,16,1099-1106. [CrossRef]
- 59. Pritchard, JK; Stephens, M.; Rosenberg, NA; Donnelly, P. Immappjar ta 'Assoċjazzjoni f'popolazzjonijiet strutturati.... Em. J. Hum. Genet. 2000, 67, 170-181. [CrossRef]
- 60. Evano, G.; Regnaut, S.; Goudet, J. Issib in-numru ta 'clusters ta' individwi li jużaw is-softwer STRUTTURA: Studju ta 'simulazzjoni.... Mol. Ekol. 2005,14, 2611-2620. [CrossRef]
- 61. Earl, D.; VonHoldt, B. STRUCTURE HARVESTER: Websajt u programm għall-viżwalizzazzjoni tal-output tal-STRUCTURE u l-implimentazzjoni tal-metodu Evano. Konserv. Genet. Riżors. 2011, 4. [CrossRef]
- 62. Takezaki, N.; Nei, M.; Tamura, K. POPTREEW: Verżjoni tal-Web ta 'POPTREE għall-kostruzzjoni ta' siġar tal-popolazzjoni minn data ta 'frekwenza ta' alleli u komputazzjoni ta 'xi kwantitajiet oħra. Mol. Biol. Evol. 2014, 31, 1622-1624. [CrossRef]
- 63. Kumar, S.; Stecher, G.; Li, M.; Knyaz, C.; Tamura, K. MEGA X. Analiżi tal-Ġenetika Evoluttiva Molekulari fuq pjattaformi tal-kompjuter. Mol. Biol. Evol. 2018, 35,1547-1549. [CrossRef]